«Integrative phylogenomics positions sponges at the root of the animal tree»,,
опубликованной в журнале Science. 390(6774):751-756.
doi: 10.1126/science.adw9456.
 © Ересковский Александр Вадимович, ведущий научный сотрудник лаборатории эволюции морфогенезов ИБР РАН. Доктор биологических наук.
© Ересковский Александр Вадимович, ведущий научный сотрудник лаборатории эволюции морфогенезов ИБР РАН. Доктор биологических наук.
Выявление наиболее базовых, древних родственных линий многоклеточных животных – один из самых важных и жарких споров в эволюционной биологии на протяжении более столетия. Решение этой загадки – ключ к пониманию биологии предков всех животных, включая то, как они перешли от одноклеточных к многоклеточным организмам и достигли поразительного разнообразия планов организации. В настоящее время эволюционные связи между видами расшифровывают, главным образом, с помощью филогеномики, которая использует компьютерные модели эволюции последовательностей для анализа больших наборов генов.
Развернутое древо жизни животных необходимо в качестве основы для построения истории генетических и морфологических изменений и появления ключевых инноваций, которые способствовали эволюционному успеху животных. Поскольку губки (тип Porifera) считаются одними из самых морфологически простых животных, они долгое время неоспоримо рассматривались и как самые древние животные. Если это так, то сложные специфичные для животных признаки, такие как нервная система, мышцы, сквозной кишечник и гонады вряд ли существовали у общего предка всех ныне живущих животных и, вероятно, впервые появились после того, как губки и другие животные дивергировали. Однако со времени первых филогеномных попыток реконструировать древо жизни животных [1] неожиданная альтернативная гипотеза получила существенную поддержку. Согласно ей гребневики (тип Ctenophora): свободноплавающие, студенистые хищники, имеющие сложно организованные ткани, нервную систему, имеющие билатеральную симметрию, мозаичное развитие, наличие трех зародышевых листков, в качестве самых древних животных [1-4]. Этот сценарий предполагает, что либо предок всех животных обладал нервной системой, мышцами и сквозным кишечником, которые позже были утрачены губками, либо у предка-животного не было этих черт, и позднее они появились независимо, по крайней мере частично, у гребневиков и у билатерий и книдарий (Рис. 1).
На протяжении последних 15-ти лет велись интенсивные споры между исследователями, отдававшими предпочтение либо губкам, либо гребневикам в качестве сестринской группы Metazoa. Попытка решить эту проблему привела к существенному прогрессу филогенетических данных, подходов и методов [1-9]. Подавляющее большинство отдельных филогенетических анализов, включая подходы, использующие «стандартный» филогенетический анализ, которые пытались избежать филогенетической ошибки, фактически всегда предоставляли сильную поддержку гребневикам как сестринской группе животных. Это привело к тому, что ряд исследователей отвергли старое (морфо-эмбриологическое) размещение губок как сестринских по отношению Metazoa, которое основывалось на гораздо меньшем количестве признаков (анализируемых единиц филогенетического анализа, т. е. гомологичных морфологических признаков или состояний нуклеотидов или аминокислот для каждого вида), которые были более субъективно отобраны и классифицированы, в пользу этого нового взгляда на филогению животных. В противоположность этому, другие специалисты утверждают, что перемещение гребневиков в положение сестринской группы является следствием систематической ошибки и что в филогенетических анализах, которые лучше всего это объясняют, они обнаружили на сотнях наборов данных однозначные подтверждения того, что губки являются самыми древними родственниками животных, а также лишь незначительные или нулевые подтверждения того, что гребневики являются сестринской группой [5, 7-9, 10].
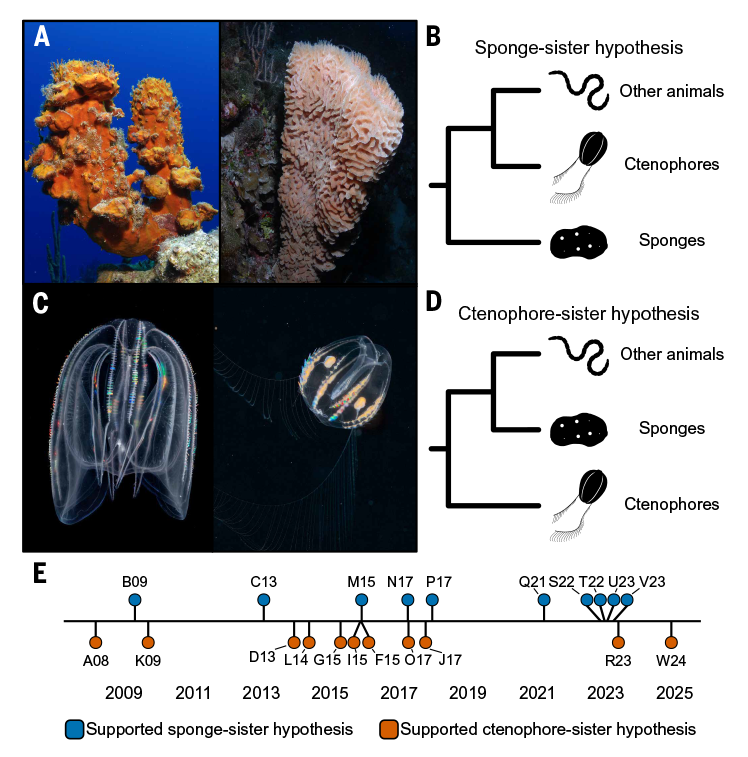
Рисунок 1. Основные конкурирующие гипотезы относительно корня филогенетического древа животных. (A) Фото двух губок. (B) Гипотеза «Porifera-first» постулирует, что губки находятся в основе древа. (C) Фото двух гребневиков. (D) Гипотеза «Ctenophora-first» постулирует, что гребневики находятся в основе древа. (E) Начиная с исследования A08 в 2008 году, различные филогенетические исследования предоставили противоречивую поддержку либо гипотезе «Porifera-first», либо гипотезе «Ctenophora-first».
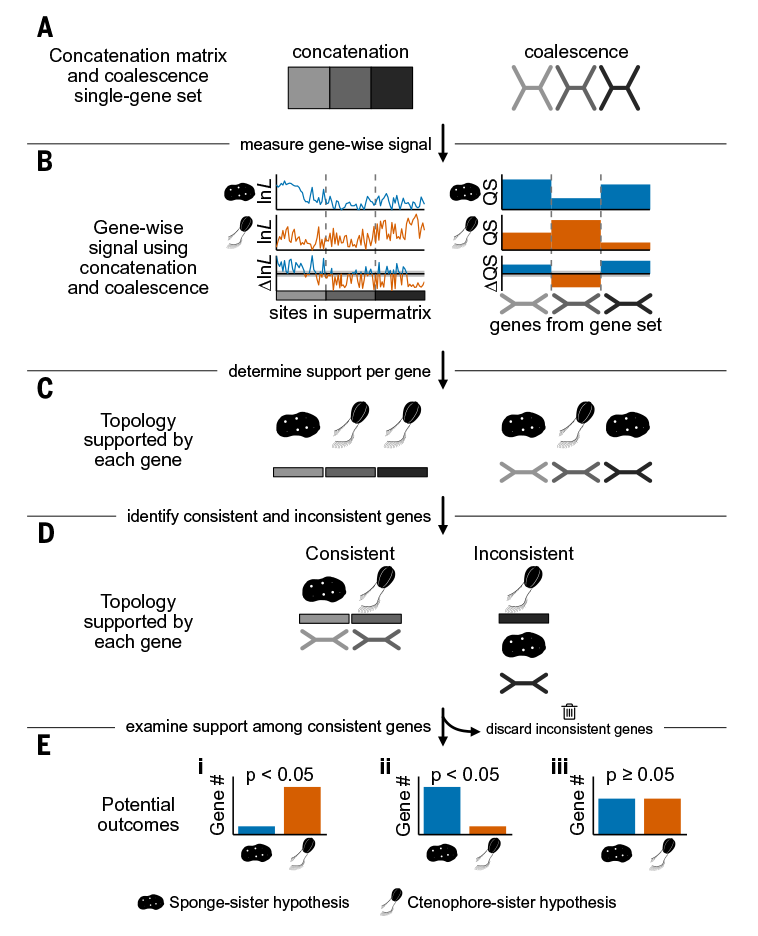
В представленной работе Steenwyk и King неожиданно предложили интегративный подход к филогеномным исследованиям. В своей работе они объединили разнообразные филогеномные методы и использовали новые доступные высококачественные данные о последовательностях из разных филогенетических линий (гребневики, губки, книдарии и голозойные микроэукариоты), чтобы найти корни дерева животных. Целью авторов было построение больших, высокоинформативных матриц филогеномных данных и их анализ с использованием интегративной филогеномики: комбинации конкатенации (множественные последовательности генов или белков объединяются в суперматрицу и анализируются с использованием подхода, основанного на полных доказательствах) и коалесценции (теория коалесценции не предполагает рекомбинации, естественного отбора, потока генов или структуры популяции, а это означает, что каждый вариант с равной вероятностью может передаваться от одного поколения к другому) (Рис. 2), а не только конкатенации или только коалесценции, как это обычно делалось в предыдущих исследованиях. Предложенная авторами интегративная филогеномика направлена на выявление надежных маркеров путем определения того, какие гены дают постоянный сигнал, независимо от того, анализируются ли они в рамках конкатенации или коалесценции. Согласованные гены подвергаются дальнейшему анализу, а несогласованные отбрасываются, поскольку, согласно результатам моделирования, они подвержены ошибкам оценки генетического дерева и неполной сортировке генеалогических линий. Более того, интегративная филогеномика позволяет преодолеть ошибки, возникающие из-за притяжения длинных ветвей (long branches attraction). Новый подход был объединен как с традиционными, так и с недавно разработанными стратегиями филогеномной субвыборки и схемами перекодирования аминокислот для выявления смещений и проверки стабильности любых выводов.
Рисунок 2. Проверка гипотез с использованием интегративного филогеномного подхода.(A) Был создан набор данных для анализа конкатенации или коалесценции, т.е. либо суперматричного выравнивания, либо набора генных деревьев соответственно. (B и C) Сигнал по генам измерялся в каждой структуре (B), и определялась топология, поддерживаемая каждым геном (C). (D) Гены, поддерживающие одну и ту же топологию с использованием обеих сред (согласованные гены), были сохранены для дальнейшего анализа; гены, конфликтующие между двумя средами (несогласованные гены), были отброшены. (E) Затем подтверждение гипотезы «Porifera-first» или «Ctenophora-first» проверялось с помощью подсчета генов, подтверждающих каждую гипотезу, и критерия хи-квадрат. Возможными результатами были: (i) что гипотеза «Ctenophora-first» или (ii) гипотеза «Porifera-first» получит значительно больше поддержки, чем другая, или (iii) что гипотезы могут быть статистически неразличимы. Синий цвет подтверждает гипотезу «Porifera-first»; оранжевый цвет подтверждает гипотезу «Ctenophora-first».
Предложенная авторами стратегия выявила беспрецедентное филогеномное подтверждение того, что губки (тип Porifera), бентосные фильтраторы, лишенные организованных тканей, являются сестринской линией по отношению ко всем остальным животным.
Почему новый метод, предложенный Steenwyk и King дал такую сильную поддержку в отношении губок как сестринских по отношению к Metazoa, тогда как предыдущие исследования застряли в филогенетическом тупике? Хотя использование огромного количества генов и аминокислот является обычным и даже ожидаемым в филогеномике, большие наборы данных также вносят свой вклад в систематические ошибки и их влияние на результаты [11]. Упор на размер набора данных может быть особенно обманчивым для коротких, древних ветвей, таких как самые глубокие в филогенетическом древе животных, где гораздо меньшее подмножество признаков (гены и аминокислоты) и на самом деле содержит изменения, имеющие отношение к рассматриваемой проблеме [12]. Большие наборы данных, которые теперь можно создавать, возможно, лучше всего использовать для извлечения небольших, обогащенных сигналом и практически безошибочных наборов, что помогает максимизировать соотношение сигнал/шум и избегать систематических ошибок при решении сложных филогенетических задач. Парадоксально, но эта версия филогеномики оказывается ближе к морфологическому анализу, поскольку использует меньшее количество признаков и несколько более субъективно отобранных.
Подобные подходы демонстрируют значительный успех как в результатах исследований Steenwyk и King, так и в других исследованиях [6,13,14], а также могут снизить вычислительные требования, что одновременно повышает воспроизводимость филогеномного анализа. Несомненно, представленный Steenwyk и King интегративный филогеномный подход вызовет критику у адептов гипотезы о том, что ктенофоры являются сестринской группой. Как предполагают Mulhair и Redmond [12], представляется возможным, хотя и маловероятным, что отбор генов с сильными сигналами, применяемый авторами, может случайно отдать приоритет генам с сильными сигналами, которые, будь то из-за действительно сложной истории или ошибок вывода, находятся в противоречии с древом вида (species tree) [15].
Выводы Steenwyk и King в очередной раз логично указывают на то, что последний общий предок животных, скорее всего, не имел нервной системы, сквозного кишечника, мышц и других организованных тканей и, следовательно, был морфологически простым. Их интегративный филогеномный подход может также иметь потенциал для решения других сложных филогенетических проблем.
Таким образом, история исследований того, кто же является сестринской группой по отношению ко всем многоклеточным животным, сделав зигзаг, вернулись на исходную позицию. Позицию, которую предложили еще в конце XIX столетия классики зоологии и сравнительной эмбриологии. Но можно ли говорить, что в данном вопросе поставлена последняя точка? Конечно нет! Вполне вероятно, что в ближайшее время будет сделан очередной ход адептов гипотезы «Ctenophora-first».
Список литературы
Dunn CW., Hejnol A, Matus DQ, Pang K, Browne WE, et al. Broad phylogenomic sampling improves resolution of the animal tree of life. Nature. 2008; 45 :745–749. DOI : https://doi.org/10.1038/nature06614
Whelan NV, Kocot KM, Moroz LL, Halanych KM. Error, signal, and the placement of Ctenophora sister to all other animals. Proc. Natl. Acad. Sci. U.S.A. 2015; 112 (18): 5773-57. https://doi.org/10.1073/pnas.1503453112
Li Y, Shen XX, Evans B, Dunn CW, Rokas A. Rooting the Animal Tree of Life. Mol. Biol. Evol. 2021; 38, 4322–4333. https://doi.org/10.1093/molbev/msab170
Schultz DT, Haddock SHD, Bredeson JV, Richard E. Green RE, Simakov O, et al. Ancient gene linkages support ctenophores as sister to other animals. Nature. 2023; 618(7963):110-117. DOI: 10.1038/s41586-023-05936-6
Redmond AK, McLysaght A. Evidence for sponges as sister to all other animals from partitioned phylogenomics with mixture models and recoding. Nat. Commun. 2021; 12, 1783. DOI: 10.1038/s41467-021-22074-7
McCarthy CGP, Mulhair PO, Siu-Tin Kg, Creevey CJ, O’Connell MJ. Improving orthologous signal and model fit in datasets addressing the root of the animal phylogeny. Mol. Biol. Evol. 2023; 40, msac276. DOI: https://doi.org/10.1093/molbev/msac276
Feuda, R., Dohrmann M, Pett W, Philippe H, et al. Improved modeling of compositional heterogeneity supports Sponges as Sister to all other Animals. Curr. Biol. 2017; 27, 3864.
Simion P, Philippe H, Baurain D, Jager M, Richter DJ, Di Franco A, et al. A large and consistent Phylogenomic Dataset supports Sponges as the Sister Group to all other animals. Curr. Biol. 2017; 27(7): 958-967. DOI: 10.1016/j.cub.2017.02.031.
Pisani D., Pett W, Dohrmann M, Feuda R, Rota-Stabellif O, Philippe H, et al. Genomic data do not support comb jellies as the sister group to all other animals. Proc. Natl. Acad. Sci. U.S.A. 2015; 112: 15402–15407. DOI : 10.1073/pnas.1518127112
Steenwyk JL, King N. The promise and pitfalls of synteny in phylogenomics. PLOS Biol. 2024; 22, e3002632. https://doi.org/10.1371/journal.pbio.3002632
Philippe H, Brinkmann H,. Lavrov DV, Timothy D, Littlewood J, et al. Resolving Difficult Phylogenetic Questions: Why More Sequences Are Not Enough PLOS Biol. 2011; 9, e1000602. https://doi.org/10.1371/journal.pbio.1000602
Mulhair PO, Redmond AK. Sponging away phylogenomic incongruence. Science. 2025; 390(6774) : 673-674. DOI :10.1126/science.aec6305
Mulhair PO, McCarthy CGP, Siu-Ting K, Creevey CJ, O’Connell MJ. Filtering artifactual signal increases support for Xenacoelomorpha and Ambulacraria sister relationship in the animal tree of life. Curr. Biol. 2022; 32, 5180. https://doi.org/10.1016/j.cub.2022.10.036
Redmond AK. Acoelomorph flatworm monophyly is a long-branch attraction artefact obscuring a clade of Acoela and Xenoturbellida. Proc. Biol. Sci. 2024; 291: 20240329. DOI : 10.1098/rspb.2024.0329
Shen XX, Steenwyk JL, Rokas A. Dissecting Incongruence between Concatenation- and Quartet-Based Approaches in Phylogenomic Data. Syst. Biol. 70, 997 (2021). DOI: 10.1093/sysbio/syab011.
Новость подготовил
© Доктор биологических наук, ведущий научный сотрудник лаборатории эволюции морфогенезов ИБР РАН. Ересковский Александр Вадимович
12.01.2026